MPprimer(Multiplex PCR primer design)用于在可靠多重 PCR 引物组合(PSC, primer set combination)约束下,从多靶标模板出发选出可同管反应的引物池:对每个模板用 Primer3 生成候选引物对,用 MFEprimer 在基因组/转录组库上评特异性,用 PriDimerCheck(PerlPrimer 思路 + 热力学)评引物二聚体,再用图扩展在兼容矩阵上选 PSC,并输出虚拟琼脂糖凝胶以检查条带可分辨性(MinBS)(BMC Bioinformatics 2010)。
文献与官方资源
| 类型 | 链接 |
|---|---|
| 论文 | Shen Z, Qu W, Wang W, et al. MPprimer: a program for reliable multiplex PCR primer design. BMC Bioinformatics 11, 143 (2010). DOI 10.1186/1471-2105-11-143 |
| 开放获取 | Springer Nature 全文 |
| GitHub | https://github.com/quwubin/MPprimer |
| 历史归档 | SourceForge mpprimer |
| 维护说明 | 作者在 About MPprimer 将 MPprimer 标为 Deprecated;多重场景更依赖一站式管线(如 MFEprimer3 MulD 等)。 |
论文中的旧主页 http://biocompute.bmi.ac.cn/MPprimer/ 多已不可用;请以 PDF + GitHub 为准。 |
应用场景
- 2×–20×+ 多重 PCR:需同时扩增多个外显子/位点(论文示例含 DMD 79 外显子 等),且要求同管内引物无强二聚体、无非特异扩增、凝胶条带可分开。
- 已有各靶标独立序列(或经预处理后的片段),希望自动组合 PSC 并给出虚拟电泳预览。
- 不适合:仅需单对引物(直接用 Primer3);或需要与论文同期 Web 服务开箱即用(维护已停,环境需自建);高相似同源区需先比对/限定区间(论文已说明)。
使用帮助
部署形态
| 方式 | 说明 |
|---|---|
| Web | 论文描述为跨平台 Web 应用;当前以能否从源码/归档成功运行为准。 |
| Standalone | Linux/Unix 独立版,便于挂载自建 BLAST 等数据库做高通量、全基因组级特异性检索。 |
| 本地依赖 | Python ≥ 2.5(论文年代);现代环境需自行评估 Python 2 兼容性或移植;需能调用 Primer3、MFEprimer、比对库等(以仓库 README 为准)。 |
输入与输出
- 典型输入
- 各靶标 DNA 序列(论文 Web 场景为 FASTA 等多序列输入);
- 特异性检索数据库:用户自备或程序配置的基因组/转录组库(Standalone 强调可换库)。
- 典型输出
- 至多 15 个 PSC(论文 Results 中 Web 默认);每 PSC 含各靶标上的 forward/reverse 及评估信息;
- 虚拟 1% 琼脂糖凝胶迁移图,用于 MinBS(minimum band spacing) 判读。
资源与环境
- 算力:靶标数 (k) 大时,候选引物对规模约 每靶 5 组 PS(Primer3 默认排序),再叠加两两二聚体与 MFEprimer 跨引物组合,复杂度随 (k) 上升;全基因组 BLAST 耗时与磁盘显著。
- 许可证:论文写明 GNU GPL v3。
功能与算法原理
1. 候选引物对(Primer3)
对每个输入模板,Primer3 默认产生 5 组候选 PS,按 penalty 升序;(k) 个模板最多 (5k) 个候选 PS。
2. 引物二聚体(PriDimerCheck)
对所有引物两两用最近邻热力学评估互补稳定性;论文采用 ΔG ≤ -7 kcal/mol 作为二聚体风险阈值量级(与程序默认策略一致,细节以源码为准)。
对引物 (a,b) 的最优二聚体构型,程序估计 (\Delta G^\circ_{a,b})(或等价评分),若
$$
\Delta G^\circ_{a,b} \le G_{\mathrm{thr}} \quad (\text{文中量级 } G_{\mathrm{thr}}=-7\ \mathrm{kcal/mol})
$$
则判为不兼容或记入惩罚(与 MPprimer 实现细节以源码为准)。
3. 特异性(MFEprimer)
- 先评正牌引物对((T_{iF}/T_{iR}))在数据库上的特异性;
- 再评跨靶标错配组合(如 (T_{iF}) 与 (T_{jF})、(T_{iF}) 与 (T_{jR}) 等 6 类 primer-pair),避免同管内非靶标扩增。
将「在库上可产生可延伸非特异产物」记为失败;若两候选引物对 (PS_u,PS_v) 在全部二聚体与特异性检验下均通过,则定义兼容。
4. 兼容图与图扩展算法
- 以候选 PS 为节点;若两 PS 无二聚体风险且无非特异扩增则连边(矩阵记 1,否则 0)。
- 图扩展:从 penalty 较低节点出发扩展,得到局部较优 PSC(非全局穷举所有组合)。
设候选引物对索引为 (u,v \in {1,\ldots,m}),定义对称兼容矩阵
$$
A_{uv} =
\begin{cases}
1, & PS_u\text{ 与 }PS_v\text{ 二聚体与特异性均兼容} \
0, & \text{否则}
\end{cases}
$$
图扩展(示意):构造无向图 (G=(V,E)),(V={PS_u}),(E={(u,v)\mid A_{uv}=1})。算法从 Primer3 penalty 较小的节点出发,在 (G) 上逐步加入与当前团/clique 兼容的节点,生成一个高权重(低 penalty)的 PSC;该过程是贪心/局部搜索,不保证全局最优。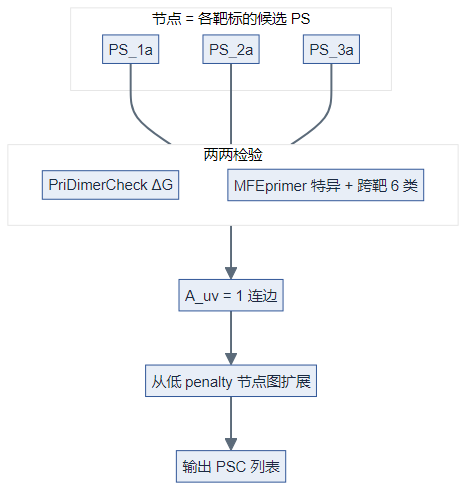
1 | flowchart TD |
5. 条带可分辨(MinBS)
引入 MinBS:按 Helling et al., 1974** 的迁移关系预测 1% 琼脂糖上条带位置,使相邻产物间距满足肉眼可区分,而非仅用固定 bp 差。
记第 (i) 个扩增子长度为 (L_i)(bp),由经验迁移曲线得到预测迁移距离 (m_i = f(L_i))(与电压、胶浓度、Marker 共标定)。MinBS 约束要求对排序后相邻条带 (i,j):
$$
\bigl| m_i - m_j \bigr| \ge \mathrm{MinBS}
$$
(f(\cdot)) 在论文中引用 Helling 关系(非线性:长片段迁移对长度差不敏感),故软件用预测距离差**而非仅用 (|L_i-L_j|)。
论文默认设计窗口(Implementation)
与 Primer3 默认未必完全一致;文中给出的默认范围包括(节选):
| 参数 | 默认 |
|---|---|
| Tm | 57–63℃ |
| 引物长度 | 18–27 bp |
| GC% | 45–55% |
| 3′ 稳定性上限 | 9.0 kcal/mol |
| Self-complementarity | 8.0 |
| 3′ self-complementarity | 3.0 |
配图(文献原图页面)
| 图号 | 内容(据摘要/图题) | 官方页面 |
|---|---|---|
| Figure 1 | MPprimer 流程与模块 | BMC — Figure 1 |
| Figure 2 | 图扩展 / 兼容示意(以期刊图题为准) | BMC — Figure 2 |
| Figure 3 | 虚拟电泳与 MinBS 相关(以期刊图题为准) | BMC — Figure 3 |
局限性
- 维护状态:官方已 Deprecated,旧 Python 2 栈与现代依赖需自行修补。
- 算法性质:图扩展为启发式,不保证全局最优 PSC。
- 数据质量:高相似序列、重复区、库版本偏旧会导致 MFEprimer 假阴/假阳;需实验验证。
- 服务可用性:历史 URL 多失效,部署以本地为主。
参考资料
- Shen Z, Qu W, Wang W, et al. BMC Bioinformatics. 2010;11:143. https://doi.org/10.1186/1471-2105-11-143
- MPprimer GitHub
- About MPprimer (status)
- MulD(作者示例): https://mfeprimer3.igenetech.com/muld
- 本站:
引物设计-03.软件-Primer3.md、引物设计-03.软件-MP-Ref.md