Publish
原文链接: CNVkit Genome-Wide Copy Number Detection and Visualization from Targeted DNA Sequencing-annotated
cnvkit.readthedocs
原理介绍PPT
CNVKit若干算法问题详解
检测原理在上述文献、PPT中已经有相对详细的介绍,此处不再进行展开。针对目前一些可视化的需求,补充记录一些关于CNVKit结果展示的相关功能和使用方法。
可视化
CNVKit提供了比较详细的可视化模块
三种可视化的主体绘图命令如下:
1 | cnvkit.py scatter -h |
scatter
说明
1 | cnvkit.py scatter Sample.cnr -s Sample.cns |
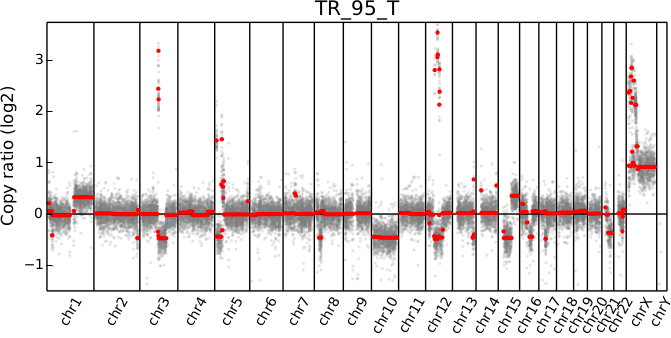
扩展参数
1 | python cnvkit.py scatter Sample.cnr |
示例
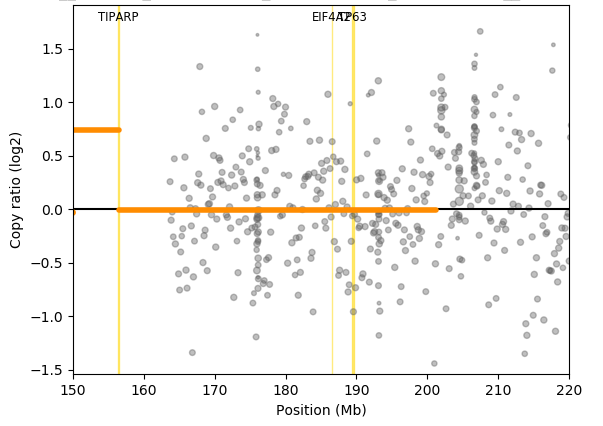
1 | /jdfstj1/B2C_COM_P1/PipeAdmin/02.software/Conda/bin/python /jdfstj1/B2C_COM_P1/PipeAdmin/04.Pipeline/01.AIO.v2.01/bin/cnvkit.py scatter ../Analyze/cnv/pancancer689__DX1790_huangrenhua_20S8320498R_20B8320498__Cancer.markdup.cnr -s ../Analyze/cnv/pancancer689__DX1790_huangrenhua_20S8320498R_20B8320498__Cancer.markdup.cns -c chr3:150000000-220000000 -g EIF4A2,TIPARP,TP63 |
diagram
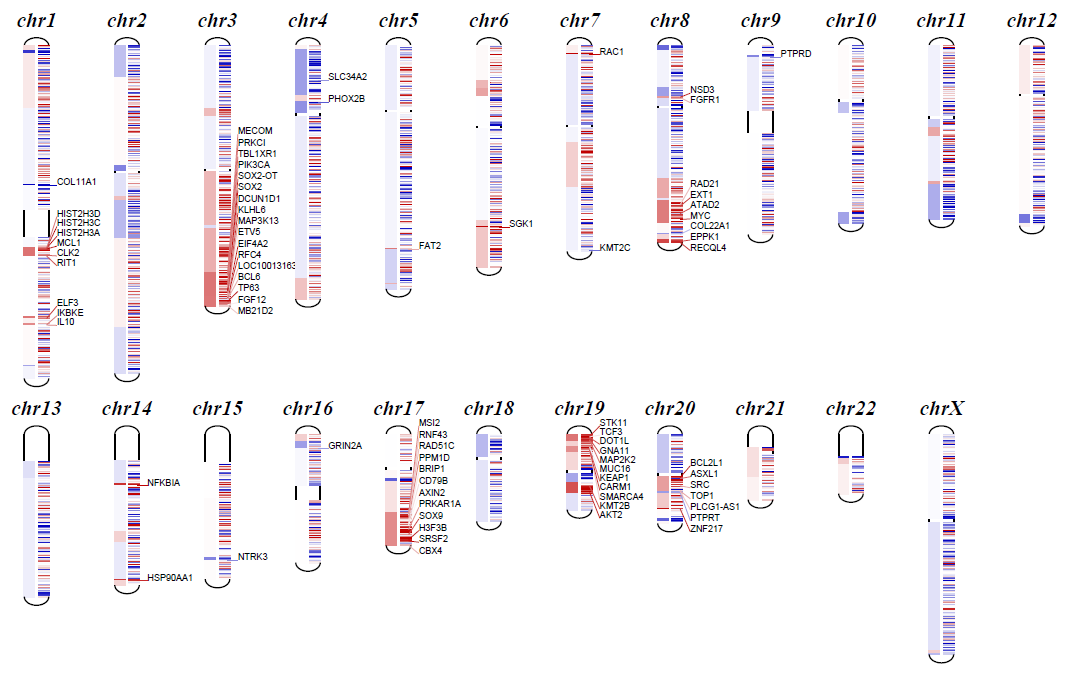
1 | python cnvkit.py diagram Sample.cnr |
结果格式说明
*.cnv
1 | chromosome, start, end, gene, log2, depth and weight |
异常处理记录
Qt载入失败
- 具体报错示例如下:
1 | Reinstalling the application may fix this problem. |
- 处理解决方案